기술통계descriptive statistics는 수집된 데이터의 특성을 요약하고 설명하는 통계 기법이다. 데이터를 대표하는 값(평균값, 중앙값, 최빈값)과 데이터의 퍼짐 정도를 나타내는 값(분산, 표준편차, 범위, 사분범위) 등을 통해 데이터의 전반적인 특성을 파악한다.
기술통계는 크게 두 가지 범주로 나뉜다.
중심 경향성: 데이터 전체를 하나의 대표값으로 요약한다.
평균값mean: 모든 값의 합을 데이터 개수로 나눈 값. 극단적인 값(이상치)에 민감하다.
중앙값median: 데이터를 크기 순으로 정렬했을 때 가운데 위치하는 값. 이상치의 영향을 별로 받지 않는다.
최빈값mode: 데이터에서 가장 빈번하게 등장하는 값. 범주형 데이터에도 적용 가능하다.
산포도: 데이터가 중심 값 주위에 얼마나 퍼져 있는지를 나타낸다.
범위range: 최댓값과 최솟값의 차이. 계산이 간단하지만 이상치에 취약하다.
분산variance: 각 값과 평균의 차이(편차)를 제곱하여 평균한 값.
표준편차standard deviation: 분산의 제곱근. 데이터와 동일한 단위를 가지며 가장 널리 쓰이는 산포 측도이다.
사분범위interquartile range, IQR: 제3사분위수(Q3)에서 제1사분위수(Q1)를 뺀 값. 중간 50% 데이터의 퍼짐 정도를 나타내며 이상치에 강건하다.
기술통계는 데이터 분석의 첫 단계로서, 탐색적 데이터 분석EDA의 핵심 요소다.
기본 설정
탐색적 데이터분석(EDA)에 필요한 핵심 라이브러리를 불러온다.
numpy: 어레이 기반 데이터 처리pandas: 데이터프레임 기반 데이터 처리matplotlib.pyplot: 데이터 시각화seaborn: 통계 기반 데이터 시각화
import numpy as np
import pandas as pd
import matplotlib.pyplot as plt
import seaborn as sns데이터프레임 내 부동소수점을 소수점 이하 6자리까지만 출력하도록 지정한다.
pd.set_option('display.precision', 6)데이터 저장소
data_url = 'https://raw.githubusercontent.com/codingalzi/code-workout-datasci/refs/heads/master/data/'17.1데이터셋 불러오기¶
body_df.csv 파일은 성인 남녀 1,000명(여성 500명, 남성 500명)의 신체 정보를 담고 있으며, 6개의 특성(변수)으로 구성된다.
| 특성 | 설명 | 타입 |
|---|---|---|
ID | 샘플 고유 식별자 (F001~F500: 여성, M001~M500: 남성) | 문자열 |
Sex | 성별 (F: 여성, M: 남성) | 범주형 |
Age | 나이 (세) | 수치형 |
Height | 키 (cm) | 수치형 |
Weight | 몸무게 (kg) | 수치형 |
Body fat percentage | 체지방률 (%) | 수치형 |
아래 그림은 데이터셋에 포함된 처음 10개 데이터와 헤더를 보여준다.
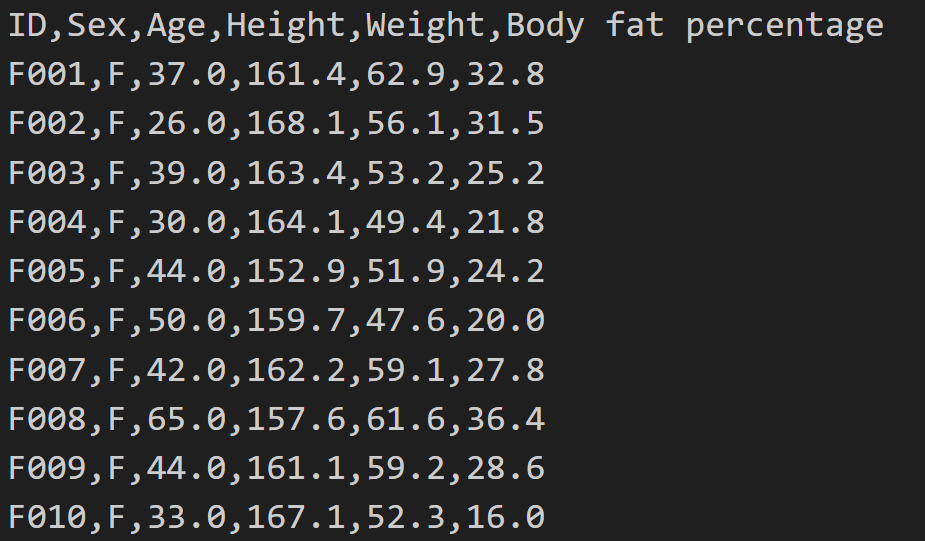
ID 특성을 행 인덱스로 지정하면서 데이터셋을 데이터프레임으로 불러온다.
body_df = pd.read_csv(data_url + "body_fat.csv", index_col='ID')불러온 데이터프레임의 처음과 끝을 확인한다. 여성 데이터 500개가 앞쪽에 위치한다.
body_df.head()남성 데이터 500개는 뒷쪽에 위치한다.
body_df.tail()info() 메서드로 각 열의 데이터 타입과 결측치 여부를 확인한다.
Sex 특성만 문자열로 구성되었다. 즉 범주형 특성이다.
나머지 특성은 모두 부동소수점 자료형을 갖는다. 즉 수치형 특성이다.
body_df.info()<class 'pandas.DataFrame'>
Index: 1000 entries, F001 to M500
Data columns (total 5 columns):
# Column Non-Null Count Dtype
--- ------ -------------- -----
0 Sex 1000 non-null str
1 Age 1000 non-null float64
2 Height 1000 non-null float64
3 Weight 1000 non-null float64
4 Body fat percentage 1000 non-null float64
dtypes: float64(4), str(1)
memory usage: 51.8 KB
Body fat percentage와 같이 띄어쓰기가 포함된 긴 열의 이름을 간결한 이름인 BFP로 변경한다. 열의 이름이 수정된 새로운 데이터프레임을 기존 변수에 재할당하는 방식으로 사용한다.
body_df = body_df.rename(columns={'Body fat percentage': 'BFP'})
body_df.info()<class 'pandas.DataFrame'>
Index: 1000 entries, F001 to M500
Data columns (total 5 columns):
# Column Non-Null Count Dtype
--- ------ -------------- -----
0 Sex 1000 non-null str
1 Age 1000 non-null float64
2 Height 1000 non-null float64
3 Weight 1000 non-null float64
4 BFP 1000 non-null float64
dtypes: float64(4), str(1)
memory usage: 51.8 KB
성별(Sex)과 같은 범주형 특성에 대해 value_counts() 메서드로 포함된 항목들의 빈도를 확인한다.
여성과 남성 정보가 각각 500개씩 포함되어 있음이 확인된다.
결과는 시리즈 객체다.
body_df['Sex'].value_counts()Sex
F 500
M 500
Name: count, dtype: int6417.2데이터 대표값¶
주어진 데이터셋을 대표하는 값으로 평균값, 중앙값, 최빈값이 가장 많이 사용된다.
17.2.1평균값¶
평균값Mean은 데이터를 모두 더한 뒤, 데이터의 개수로 나눈 값을 말한다. 데이터셋이 개의 데이터 로 이루어져 있다면 이 데이터셋의 평균값 는 다음과 같이 구한다.
예를 들어, 성인 남녀 1000명의 평균키는 다음과 같다.
body_df['Height'].mean()np.float64(164.8117)17.2.2중앙값¶
중앙값은 데이터를 크기 순서대로 나열할 때 정확히 중앙에 위치한 값이다.
body_df['Height'].median()np.float64(164.3)17.2.3최빈값¶
최빈값은 데이터에서 가장 많이 나타나는 값이다.
키 데이터처럼 연속형 데이터의 경우, 동일한 값이 여러 번 나타나는 경우가 드물 수 있다.
데이터프레임의 mode() 메서드를 이용하여 최빈값을 확인할 수 있다.
키의 경우 162.5와 163.1의 빈도가 가장 높다고 확인된다.
body_df['Height'].mode()0 159.1
1 163.1
Name: Height, dtype: float64value_counts() 메서드를 이용하면 빈도도 확인된다.
163.1과 159.1이 각각 10번씩 가장 많이 사용되었다.
body_df['Height'].value_counts().iloc[:10]Height
163.1 10
159.1 10
162.5 9
161.0 8
167.3 8
163.7 8
170.2 8
172.8 8
160.5 7
163.2 7
Name: count, dtype: int6417.3데이터 분포¶
17.3.1편차¶
각 데이터가 평균으로부터 떨어져 있는 정도를 편차deviation라 한다. 즉, 편차는 데이터들이 평균값으로부터 떨어져 있는 정도를 나타내는 값이다.
deviation = body_df['Height'] - body_df['Height'].mean()
deviationID
F001 -3.4117
F002 3.2883
F003 -1.4117
F004 -0.7117
F005 -11.9117
...
M496 11.5883
M497 -7.4117
M498 2.4883
M499 5.0883
M500 8.8883
Name: Height, Length: 1000, dtype: float64편차의 평균값은 항상 0 임에 주의한다. 아래 코드의 결과가 0이 아닌 0에 매우 가까운 값으로 계산되는 이유는 부동소수점 연산의 한계임에 주의한다.
deviation.mean()np.float64(-1.8189894035458565e-15)17.3.2분산¶
앞서 보았듯이 데이터들의 편차는 항상 음수와 양수가 섞여 평균값이 0이 되기에 데이터들이 평균값을 기준으로 얼마나 떨어져 있는지를 나타내는 측정값으로는 적절치 않다. 이러한 용도로 쓰이는 값이 바로 지금부터 소개할 분산variance과 표준편차standard deviation이다.
분산variance은 편차의 제곱의 평균값이며, 계산식은 다음과 같다.
body_df['Height']에 포함된 키 데이터의 분산은 편차의 제곱에 mean() 메서드를 적용해 구할 수 있다.
(deviation ** 2).mean()np.float64(73.00429310999999)데이터프레임의 var() 메서드를 활용해 구해도 된다.
하지만 데이터프레임을 이용할 때는 ddof=0 키워드 인자를 사용해 (편향된) 표본분산sample variance을 계산토록 해야한다.
s2 = body_df['Height'].var(ddof=0)
s2np.float64(73.00429310999999)ddof 키워드 인자를 생략하면 ddof=1로 지정된 기본 옵션이 실행되며
불편분산unbiased variance, 즉 편향되지 않은 표본분산을 계산한다.
불편분산은 편향분산biased variance보다 좀 더 크다.
body_df['Height'].var()np.float64(73.07737048048048)17.3.3표준편차¶
분산은 편차 제곱의 평균값이므로, 데이터의 단위가 다르다. 따라서 동일한 단위로 데이터의 분포도를 측정하는 용도로 분산의 제곱근인 표준편차standard deviation를 활용한다.
데이터프레임의 std() 메서드를 사용하여 표준편차를 구한다.
하지만 분산의 경우처럼 ddof=0 옵션을 함께 지정해야 편향분산에 근거한 표준편차를 계산한다.
s = body_df['Height'].std(ddof=0)
snp.float64(8.54425497688359)불편분산에 근거한 표준편차는 다음과 같다.
body_df['Height'].std(ddof=1)np.float64(8.548530311140066)17.3.4범위¶
범위range는 데이터의 최댓값과 최솟값의 차이를 가리킨다.
body_df['Height']에 포함된 데이터의 범위는 다음과 같이 구한다.
range = body_df['Height'].max() - body_df['Height'].min()
rangenp.float64(45.39999999999998)17.3.5사분위수와 사분범위¶
범위는 최댓값과 최소값이 변하면 그에 따라 값이 크게 요동칠 수 있다. 따라서 데이터 분포를 이해하는 데는 범위 대신 데이터의 변화에 덜 민감한 사분위수와 사분범위가 주로 이용된다.
데이터의 하위 25%, 50%, 75%에 위치하는 값을
각각 제1사분위수(Q1), 제2사분위수(Q2), 제3사분위수(Q3)라 한다.
Q2는 앞서 살펴본 중앙값에 해당한다.
사분범위interquartile range는 제3사분위수에서 제1사분위수를 뺀 값으로서, 중앙값을 중심으로 50%의 데이터가 모여있는 구간의 크기를 나타낸다.
아래 코드는 body_df['Height']의 사분범위를 계산한다.
Q1 = body_df['Height'].quantile(0.25)
Q3 = body_df['Height'].quantile(0.75)
IQR = Q3 - Q1
IQRnp.float64(13.025000000000006)17.3.6상자 그림¶
상자 그림은 다음 값들을 점, 선분, 직사각형 등으로 표시하는데, 그림에 표시되는 값들을 위에서부터 나열하면 다음과 같다.
너무 큰 이상치outlier에 해당하는 점들
(Q3 + 1.5 * IQR)에 해당하는 값의 수평 선분
Q3, Q2, Q1에 해당하는 값을 이용한 직사각형
(Q1 - 1.5 * IQR)에 해당하는 값의 수평 선분
너무 작은 이상치outlier에 해당하는 점들
이제 데이터프레임 body_df의 boxplot() 메서드를 이용하여 Height 특성에 포함된 값들을 대상으로 상자 그림을 그리면, 키의 경우엔 IQR 기준 이상치가 없다.
boxplot() 함수의 인자로 사용된 값들은 다음과 같다.
column=['Height']: 상자 그림을 그릴 대상 열 (Height 특성)grid=False: 배경 격자표시 표시 여부 (여기서는 표시하지 않도록 설정)flierprops=dict(...): 이상치를 표시하는 점의 스타일 (모양marker, 색상markerfacecolor, 크기markersize지정)
body_df.boxplot(
column=['Height'],
grid=False,
flierprops=dict(marker='o', markerfacecolor='red', markersize=5)
)
plt.show()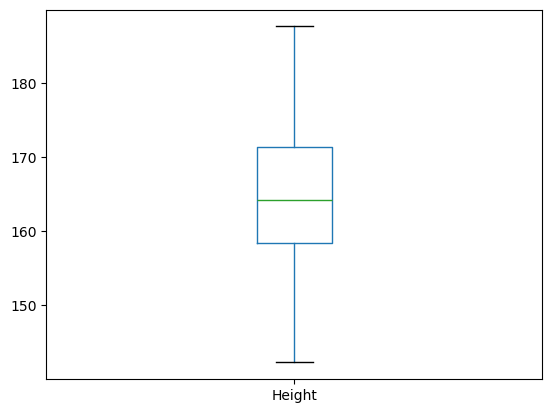
반면에 체중 데이터에는 IQR 기준 이상치가 존재한다.
body_df.boxplot(
column=['Weight'],
grid=False,
flierprops=dict(marker='o', markerfacecolor='red', markersize=5)
)
plt.show()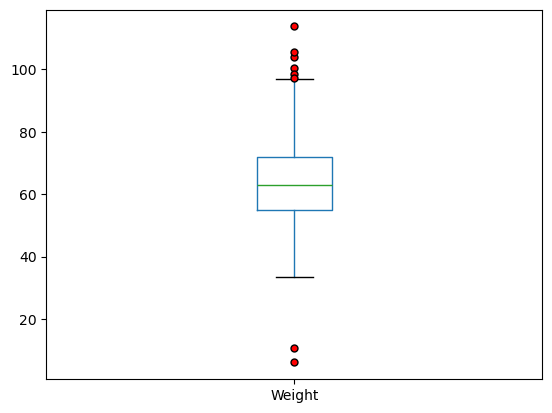
17.3.7히스토그램¶
상자 그림은 사분위수와 이상치를 파악하는 데는 용이하지만, 데이터의 전체적인 윤곽과 세부 분포를 직관적으로 파악하기에는 한계가 있다. 이럴 때 히스토그램histogram을 활용하면 데이터를 특정 범위의 구간(bins) 단위로 나눈 뒤, 각 구간에 속하는 데이터의 빈도(개수)를 막대로 표시하여 데이터 분포의 전반적인 형태를 한눈에 살펴볼 수 있다.
데이터프레임의 hist() 메서드(또는 Matplotlib의 hist())를 활용하면 손쉽게 히스토그램을 그릴 수 있다. 히스토그램의 구간(bins) 개수나 너비를 조정하는 구체적인 설정 방법은 나중에 자세히 다룬다.
body_df['Height'].hist(bins=20, edgecolor='black', grid=False)
plt.xlabel('Height')
plt.ylabel('Frequency')
plt.title('Height Distribution')
plt.show()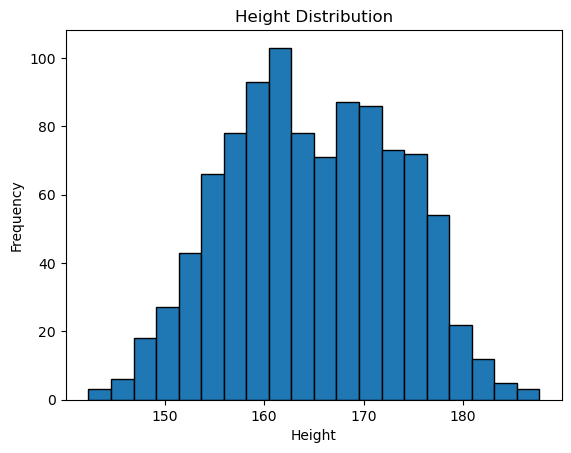
히스토그램의 막대 개수를 고정(위 코드에서는 bins=20)하는 방식 외에도, 아래와 같이 데이터의 범위를 기준으로 직접 막대의 구간(bins) 간격을 설정하여 나타낼 수도 있다. 여기서는 np.arange()를 활용해 관측된 키의 최솟값에서 5 작고, 최댓값에서 5 큰 범위 내에서 5의 간격을 가지는 구간들의 경곗값을 생성한다.
bins = np.arange(body_df['Height'].min() - 5, body_df['Height'].max() + 5, 5)
body_df['Height'].hist(bins=bins, edgecolor='black', grid=False)
plt.xlabel('Height')
plt.ylabel('Frequency')
plt.title('Height Distribution')
plt.show()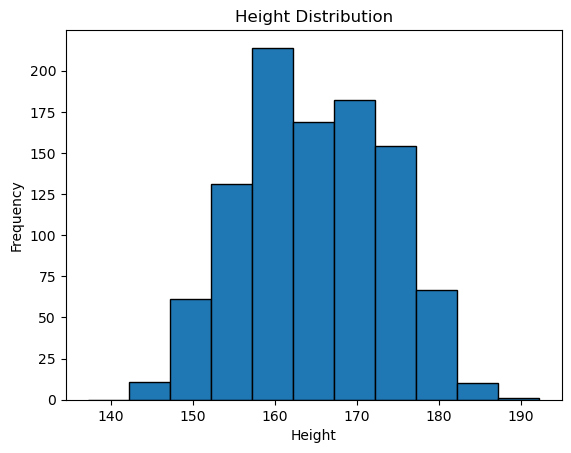
시각화를 위한 seaborn 라이브러리를 활용하면 분포를 보다 세련된 형태로 손쉽게 파악할 수 있다. sns.histplot() 함수를 호출하여 동일한 히스토그램을 그릴 수 있다.
import seaborn as sns
sns.histplot(data=body_df, x='Height', bins=20, alpha=0.6)
plt.title('Height Distribution')
plt.show()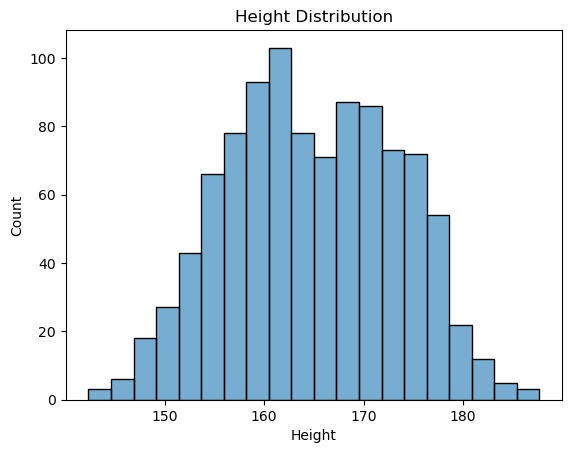
sns.histplot() 함수의 bins 매개변수의 키워드 인자를 지정하여
x-축의 범위와 구간 크기를 원하는 대로 조정할 수 있다.
import seaborn as sns
bins = np.arange(body_df['Height'].min() - 5, body_df['Height'].max() + 5, 5)
sns.histplot(data=body_df, x='Height', bins=bins, alpha=0.6)
plt.title('Height Distribution')
plt.show()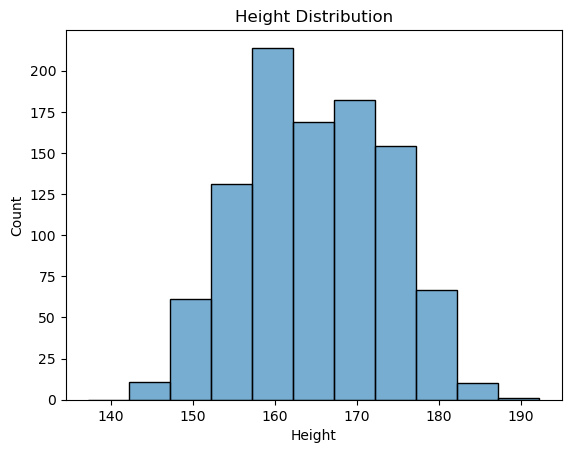
17.3.8기술통계 종합¶
데이터프레임의 describe() 메서드는
데이터의 개수, 평균값, 표준편차, 최댓값, 최소값, 사분위수에 대한 정보를 담고 있는 데이터프레임을 생성한다. 지금까지 개별적으로 살펴본 통계량을 한번에 확인할 수 있어 매우 유용하다.
단, 표준편차가 불편분산에 근거한 값임에 주의한다.
body_df['Height'].describe()count 1000.00000
mean 164.81170
std 8.54853
min 142.30000
25% 158.40000
50% 164.30000
75% 171.42500
max 187.70000
Name: Height, dtype: float64지금까지 키 데이터로 각 기술통계량의 의미와 계산 방법을 익혔다.
이제 body_df 데이터프레임 전체에 describe() 메서드를 적용하면 1000명의 모든 수치형 특성(나이, 키, 몸무게, 체지방률)에 대한 기술통계를 한번에 확인할 수 있다.
body_df.describe()17.4그룹별 기술통계¶
범주형 변수를 기준으로 데이터를 나누어 그룹별 기술통계를 확인하면 집단 간의 특성과 차이를 더 깊이 이해할 수 있다.
body_df 데이터프레임의 경우, 성별(Sex) 변수를 기준으로 groupby() 메서드를 활용하면 남성과 여성 그룹의 특성을 각각 비교할 수 있다.
먼저 각 성별 데이터의 수(데이터 개수)와 비율을 확인해본다.
body_df.groupby('Sex').size()Sex
F 500
M 500
dtype: int64body_df.groupby('Sex').size() / len(body_df)Sex
F 0.5
M 0.5
dtype: float64이어서 각 변수에 대해 성별 평균을 산출한다.
body_df.groupby('Sex').mean()다양한 기술 통계(평균, 표준편차, 최소, 최대값)를 한 번에 보고 싶다면 agg() 메서드를 사용한다.
body_df.groupby('Sex').agg(['mean', 'std', 'min', 'max'])다중 인덱스를 사용하는 행 또는 열에 대한 인덱싱은 인덱스로 구성된 튜플을 사용하면 된다. 예를 들어, 아래 코드는 나이의 성별 평균값을 확인한다.
df_double_index = body_df.groupby('Sex').agg(['mean', 'std', 'min', 'max'])
df_double_index.loc[:, ('Age', 'mean')]Sex
F 49.030
M 47.324
Name: (Age, mean), dtype: float64컬럼별로 서로 다른 집계 함수를 적용하는 것 또한 agg() 메서드로 가능하다.
body_df.groupby('Sex').agg({'Height': 'mean', 'Weight': 'median', 'BFP': 'std'})기술통계 조건에 따라 그룹을 걸러내고 싶다면 groupby() 객체에 filter() 메서드를 사용한다. 예를 들어 전체 평균 키가 대상이 아니라 "평균 키가 170cm 이상인 그룹(여기서는 남성)"만 남기도록 필터링할 수 있다.
# 평균 키가 170 이상인 그룹만 유지
body_df.groupby('Sex').filter(lambda g: g['Height'].mean() >= 170)기술통계 수치로만 비교가 어렵다면 상자 그림(boxplot) 등 시각적 자료를 함께 사용하는 것이 효과적이다.
boxplot() 메서드에 by 인자를 지정하면 성별과 같은 범주형 변수를 기준으로 수치들의 분포 범위를 보다 직관적으로 비교할 수 있다.
키 데이터에서 성별 구분을 하면 IQR 기준 이상치가 포함되어 있음이 확인된다. 이렇듯 동일한 데이터에 대해서 처리방식에 따라 결과가 달라질 수 있음에 주의한다.
body_df.boxplot(
column=['Height', 'Weight', 'BFP'],
by='Sex',
layout=(1, 3),
figsize=(12, 4),
grid=False,
sharey=False,
flierprops=dict(marker='o', markerfacecolor='red', markersize=4)
)
plt.suptitle('')
plt.tight_layout()
plt.show()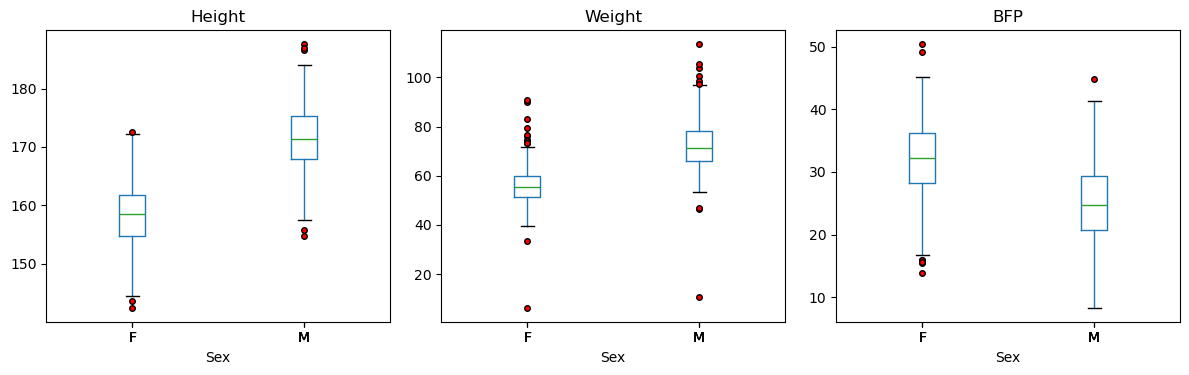
마찬가지로 성별에 따른 키의 분포를 히스토그램으로 시각화하여 겹쳐볼 수 있다.
이를 위해 seaborn 라이브러리의 histplot()을 활용하면 더욱 직관적이고 깔끔한 그룹별 히스토그램을 작성할 수 있다. hue 인자에 기준이 될 범주형 변수를 전달해주면 그룹별 분포가 겹쳐서 출력된다.
import seaborn as sns
sns.histplot(data=body_df, x='Height', hue='Sex', bins=20, alpha=0.6)
plt.title('Height Distribution by Sex')
plt.show()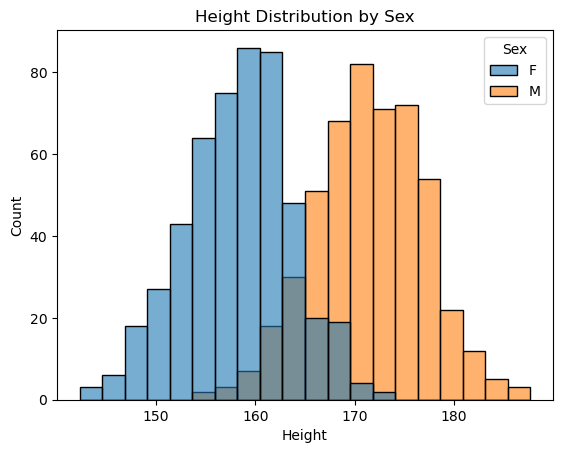
17.5기술통계량 활용¶
17.5.1이상치 탐지¶
이상치outlier는 다른 데이터와 현저히 다른 값으로, 분석 결과를 왜곡할 수 있다. IQR을 이용한 이상치 탐지는 가장 널리 쓰이는 방법이다.
이상치 기준: Q1 - 1.5 × IQR 미만이거나 Q3 + 1.5 × IQR 초과인 값
이 범위를 울타리fence라 부르며, 상자 그림의 수염(whisker) 끝이 이 위치에 해당한다.
body_df의 몸무게(Weight) 데이터에 포함된 이상치를 확인한다. 먼저 사분위수와 울타리 값을 계산한다.
Q1 = body_df['Weight'].quantile(0.25)
Q3 = body_df['Weight'].quantile(0.75)
IQR = Q3 - Q1
lower = Q1 - 1.5 * IQR
upper = Q3 + 1.5 * IQR
print(f'Q1: {Q1}, Q3: {Q3}, IQR: {IQR}')
print(f'하한 울타리: {lower:.2f}')
print(f'상한 울타리: {upper:.2f}')Q1: 55.075, Q3: 71.92500000000001, IQR: 16.85000000000001
하한 울타리: 29.80
상한 울타리: 97.20
울타리 범위를 벗어난 행을 불리언 인덱싱으로 추출한다.
weights_df = body_df['Weight']
mask = (weights_df < lower) | (weights_df > upper)
weights_df[mask]ID
F470 6.0
M042 10.8
M208 100.5
M210 103.9
M218 113.8
M331 98.5
M342 97.4
M360 105.6
Name: Weight, dtype: float64이상치를 포함한 데이터 샘플을 제거한 데이터프레임을 만들고, 제거 전후의 평균값을 비교한다. 평균값은 조금 달라진 반면에 중앙값은 그대로다.
weights_df.mean()np.float64(64.13860000000001)weights_clean = weights_df[~mask]
print(f'이상치 제거 전 평균: {weights_df.mean():.4f}')
print(f'이상치 제거 후 평균: {weights_clean.mean():.4f}')
print()
print(f'이상치 제거 전 중앙값: {weights_df.median():.4f}')
print(f'이상치 제거 후 중앙값: {weights_clean.median():.4f}')이상치 제거 전 평균: 64.1386
이상치 제거 후 평균: 64.0142
이상치 제거 전 중앙값: 62.8000
이상치 제거 후 중앙값: 62.8000
성별 그룹별로 이상치 제거 전후의 평균값과 중앙값을 비교하면, 평균값에 비해 중앙값의 변화가 상대적으로 매우 작음에 주의한다.
sex_weight_df = body_df[['Sex', 'Weight']]
print('=== 이상치 제거 전 ===')
print(sex_weight_df.groupby('Sex')['Weight'].agg(['mean', 'median']))
print()
print('=== 이상치 제거 후 ===')
print(sex_weight_df[~mask].groupby('Sex')['Weight'].agg(['mean', 'median']))=== 이상치 제거 전 ===
mean median
Sex
F 56.0244 55.3
M 72.2528 71.4
=== 이상치 제거 후 ===
mean median
Sex
F 56.124649 55.3
M 71.999797 71.2
17.5.2데이터 정규화¶
body_df.describe()기술통계량(평균, 표준편차, 최댓값, 최솟값)은 데이터를 요약하는 것 외에도 데이터를 변환하는 데 직접 활용된다. 데이터의 특성마다 단위와 범위가 다르면 직접 비교하거나 분석 모델에 함께 사용하기 어렵다. 예를 들어, 키는 128~205 범위의 값이고 체지방률은 8~50 범위의 값이기에 두 특성의 값을 일대일로 비교하기는 어렵다. 이런 경우 데이터를 정규화normalization하여 특성값들의 범위를 통일시키는 기법을 적용한다. 대표적인 정규화 기법으로 min-max 스케일링과 표준화(z-score)가 있다.
min-max 스케일링
min-max 스케일링은 데이터의 최솟값을 0, 최댓값을 1로 맞추어 모든 값을 0과 1 사이로 변환하는 기법이다. 현재 데이터 값이 전체 데이터 구간(최댓값 - 최솟값)에서 차지하는 상대적인 위치를 비율로 계산하며, 수식은 다음과 같다.
여기서 는 원래 데이터 값, 와 는 각각 가 속한 데이터셋의 최솟값과 최댓값을 가리킨다.
body_df의 키 데이터에 min-max 스케일링을 적용한다.
height_col = body_df[['Height']]
height_minmax = (height_col - height_col.min()) / (height_col.max() - height_col.min())
body_df['Height_minmax'] = height_minmax
body_df['Height_minmax']ID
F001 0.420705
F002 0.568282
F003 0.464758
F004 0.480176
F005 0.233480
...
M496 0.751101
M497 0.332599
M498 0.550661
M499 0.607930
M500 0.691630
Name: Height_minmax, Length: 1000, dtype: float64변환된 데이터의 최솟값은 0, 최댓값은 1이 된다.
body_df.describe()표준화
표준화는 데이터의 평균을 0, 표준편차를 1로 맞추어 변환하는 기법이다. 변환된 데이터 값을 z-점수z-score라고 부르며, 각 데이터 값이 평균으로부터 표준편차의 몇 배만큼 떨어져 있는지를 나타낸다. 수식은 다음과 같다.
여기서 는 원래 데이터 값, 와 는 가 속한 데이터셋의 평균값과 표준편차를 가리킨다.
body_df의 키 데이터에 표준화 스케일링을 적용한다.
height_z = (height_col - height_col.mean()) / height_col.std(ddof=0)
body_df['Height_z'] = height_z
body_df['Height_z']ID
F001 -0.399298
F002 0.384855
F003 -0.165222
F004 -0.083296
F005 -1.394118
...
M496 1.356268
M497 -0.867448
M498 0.291225
M499 0.595523
M500 1.040266
Name: Height_z, Length: 1000, dtype: float64변환된 데이터의 평균값과 표준편차가 각각 0과 1(에 매우 가까운 값)이 된다.
body_df.describe()17.6연습문제¶
문제 1: 기술통계
iris.csv 파일은 통계학자 피셔(R. A. Fisher)가 1936년에 발표한 붓꽃(Iris) 데이터셋으로, 세 품종의 붓꽃(Setosa, Versicolor, Virginica) 각 50개씩 총 150개 샘플에 대한 네 가지 수치 측정값과 품종 문자열을로 구성된 범주형 특성을 담고 있다.
| 특성 | 설명 | 타입 |
|---|---|---|
sepal.length | 꽃받침 길이 (cm) | 수치형 |
sepal.width | 꽃받침 너비 (cm) | 수치형 |
petal.length | 꽃잎 길이 (cm) | 수치형 |
petal.width | 꽃잎 너비 (cm) | 수치형 |
variety | 품종 (Setosa, Versicolor, Virginica) | 범주형 |
iris_df = pd.read_csv(data_url + 'iris.csv')
iris_df데이터프레임의 기본 정보를 확인한다.
iris_df.info()<class 'pandas.DataFrame'>
RangeIndex: 150 entries, 0 to 149
Data columns (total 5 columns):
# Column Non-Null Count Dtype
--- ------ -------------- -----
0 sepal.length 150 non-null float64
1 sepal.width 150 non-null float64
2 petal.length 150 non-null float64
3 petal.width 150 non-null float64
4 variety 150 non-null str
dtypes: float64(4), str(1)
memory usage: 7.2 KB
(1) petal.length의 평균을 계산하라.
답:
판다스 시리즈의 .mean() 메서드를 사용하여 petal.length 열의 평균을 구한다.
iris_df['petal.length'].mean()np.float64(3.7580000000000005)(2) sepal.width의 중앙값을 계산하라.
답:
.median() 메서드는 데이터를 크기순으로 정렬했을 때 가운데 위치하는 값을 반환한다.
iris_df['sepal.width'].median()np.float64(3.0)(3) petal.width에서 가장 빈번하게 등장하는 값(최빈값)을 하나 구하라.
답:
판다스 시리즈의 .mode() 메서드는 최빈값을 시리즈로 반환한다. 최빈값이 여러 개일 수 있으므로 인덱스 [0]으로 첫 번째 값을 꺼낸다.
iris_df['petal.width'].mode()[0]np.float64(0.2)(4) sepal.length의 제1, 제3 사분위수와 사분범위(IQR)를 계산하라.
답:
.quantile() 메서드에 0.25와 0.75를 지정하여 제1, 제3 사분위수를 구한다. IQR은 Q3 - Q1이다.
Q1 = iris_df['sepal.length'].quantile(0.25)
Q3 = iris_df['sepal.length'].quantile(0.75)
IQR = Q3 - Q1
print(f"Q1: {Q1}, Q3: {Q3}, IQR: {IQR}")Q1: 5.1, Q3: 6.4, IQR: 1.3000000000000007
(5) sepal.width에 대한 상자 그림을 그려라.
답:
.boxplot() 메서드를 활용한다.
iris_df.boxplot(
column=['sepal.width'],
grid=False,
flierprops=dict(marker='o', markerfacecolor='red', markersize=5)
)
plt.show()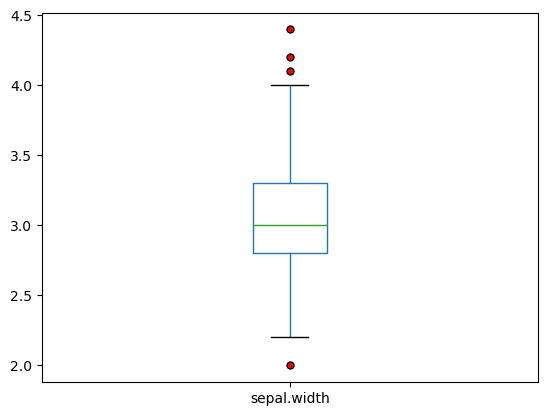
(6) petal.width의 범위, 분산(편향), 표준편차(편향)를 계산하라.
답:
범위는 .max() - .min()으로 구한다. 판다스의 .var()와 .std()는 기본적으로 비편향(ddof=1)을 사용하므로, 편향 분산/표준편차를 구하려면 ddof=0을 지정한다.
pw = iris_df['petal.width']
print(f"범위: {pw.max() - pw.min()}")
print(f"분산: {pw.var(ddof=0)}")
print(f"표준편차: {pw.std(ddof=0)}")범위: 2.4
분산: 0.5771328888888888
표준편차: 0.7596926279021594
(7) petal.length를 min-max 스케일링하여 petal_length_scaled 열로 데이터프레임에 추가하라.
답:
(x - min) / (max - min) 공식을 판다스 시리즈 연산으로 적용한 뒤, 결과를 새 열로 추가한다.
pl = iris_df['petal.length']
iris_df['petal_length_scaled'] = (pl - pl.min()) / (pl.max() - pl.min())
iris_df[['petal.length', 'petal_length_scaled']].head()(8) sepal.width를 표준화(Z-score)하여 sepal_width_z 열로 데이터프레임에 추가하라.
답:
(x - mean) / std 공식으로 Z-score를 계산한다. 편향 표준편차(ddof=0)를 사용한다.
sw = iris_df['sepal.width']
iris_df['sepal_width_z'] = (sw - sw.mean()) / sw.std(ddof=0)
iris_df[['sepal.width', 'sepal_width_z']].head()(9) sepal.width에서 IQR 기반 이상치를 탐지하라. 이상치의 개수와 해당 행을 출력하라.
답:
IQR 기반 이상치 판별 기준: Q1 - 1.5×IQR 미만이거나 Q3 + 1.5×IQR 초과인 값을 이상치로 간주한다. 불리언 인덱싱으로 해당 행을 추출한다.
sw = iris_df['sepal.width']
Q1 = sw.quantile(0.25)
Q3 = sw.quantile(0.75)
IQR = Q3 - Q1
lower = Q1 - 1.5 * IQR
upper = Q3 + 1.5 * IQR
outliers = iris_df[(sw < lower) | (sw > upper)]
print(f"이상치 개수: {len(outliers)}")
outliers이상치 개수: 4
(10) petal.length의 히스토그램을 그려라. 적절한 구간(bins)을 설정할 것.
답:
plt.hist()로 히스토그램을 그린다. np.arange()를 사용하여 데이터 범위에 맞는 구간을 설정한다.
pl = iris_df['petal.length']
bins = np.arange(pl.min(), pl.max() + 0.5, 0.5)
plt.hist(pl, bins=bins, edgecolor='black')
plt.xlabel('Petal Length (cm)')
plt.ylabel('Frequency')
plt.title('Petal Length Histogram')
plt.show()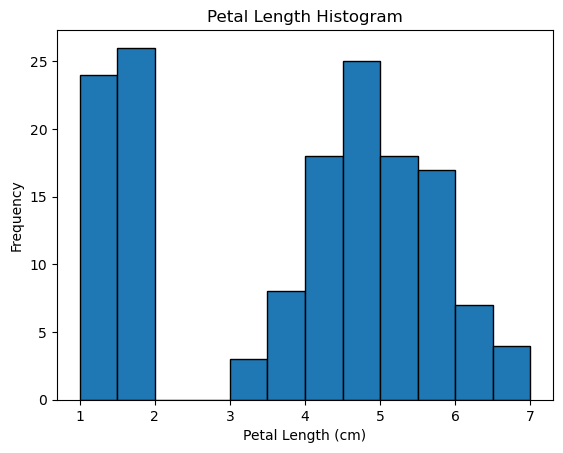
문제 2: 그룹별 기술통계
groupby() 메서드를 활용하여 붓꽃 데이터셋(iris_df)의 품종(variety)별 기술통계를 구한다.
(1) variety 컬럼을 기준으로 품종별 샘플 수를 구하라.
답:
groupby('variety').size()는 variety 컬럼을 기준으로 그룹을 만들고 각 그룹의 행 수를 반환한다.
iris_df.groupby('variety').size()variety
Setosa 50
Versicolor 50
Virginica 50
dtype: int64(2) 품종별 모든 수치형 변수의 평균을 구하라.
답:
groupby('variety').mean(numeric_only=True)는 품종별로 수치형 변수 전체의 평균을 계산하여 데이터프레임으로 반환한다.
iris_df.groupby('variety').mean(numeric_only=True)(3) 품종별 petal.length의 평균, 표준편차, 최솟값, 최댓값을 구하라.
답:
groupby('variety')['petal.length'].agg([...])는 petal.length 열을 품종별로 그룹화한 뒤 지정한 여러 통계량을 한 번에 계산한다.
iris_df.groupby('variety')['petal.length'].agg(['mean', 'std', 'min', 'max'])(4) describe() 메서드를 사용하여 품종별 sepal.length의 기술통계를 구하라.
답:
groupby('variety')['sepal.length'].describe()는 sepal.length 열을 품종별로 그룹화한 뒤 개수·평균·표준편차·최솟값·사분위수·최댓값 등 기본 기술통계를 한 번에 출력한다.
iris_df.groupby('variety')['sepal.length'].describe()문제 3: 넘파이 어레이 활용 기술통계 분석
기술통계는 넘파이 어레이만으로도 충분히 할 수 있음을 이번 문제에서 보여준다.
문제 설정을 위해 기본 데이터 저장소에 있는 sc_weir.csv 파일을 활용한다.
이 데이터는 광주광역시에서부터 전라남도 나주를 거쳐 서해까지 이어지는 영산강에 설치된 승촌보에서 측정한 두 종류의 데이터를 담고 있다.
Chl-a: 녹조 발생의 주요 요인인 클로로필-A 수치 100개Discharge: 보에서 방출되는 시간당 방류량 수치 100개
이 데이터를 수집한 목적은 클로로필-A의 농도와 보 방류량과의 상관관계를 확인하기 위함이다. 일반적으로 방류량이 많을수록 클로로필-A 농도는 떨어지며, 반대로 클로로필-A 농도가 높을수록 수질(water quality)이 나빠진다.
sc_weir_df = pd.read_csv(data_url+'sc_weir.csv')
sc_weir_df데이터프레임의 values 속성은 행과 열의 정보를 제외한 항목들로만 구성된
동일한 모양의 넘파이 어레이를 가리킨다.
sc_weir_arr = sc_weir_df.values변환된 넘파이 어레이의 형태(행 수, 열 수)를 확인한다.
sc_weir_arr.shape(100, 2)처음 10개의 항목은 다음과 같다.
sc_weir_arr[:10]array([[51, 25],
[51, 25],
[53, 24],
[53, 24],
[54, 22],
[55, 22],
[57, 21],
[57, 21],
[59, 20],
[60, 20]])(1) 방류량의 평균값을 계산하라.
답:
방류량은 1번 열의 데이터다.
discharge_arr = sc_weir_arr[:, 1]np.mean() 함수를 사용하여 방류량 어레이의 평균을 구한다.
np.mean(discharge_arr)np.float64(14.93)(2) 방류량의 중앙값을 계산하라.
답:
np.median() 함수를 사용하여 방류량 어레이의 중앙값을 구한다.
np.median(discharge_arr)np.float64(13.0)(3) 방류량의 최빈값을 계산하라.
답:
넘파이에는 최빈값을 단독으로 구하는 함수가 없다. 대신 np.unique() 함수를 이용해 개별 값과 빈도수를 추출한 뒤 가장 큰 빈도를 가지는 값을 찾을 수 있다.
np.unique(..., return_counts=True) 함수를 호출하면, 어레이 내에 존재하는 고유한 값들의 어레이와
해당 값들이 등장하는 빈도 어레이를 튜플 형태로 반환한다.
이를 활용해 빈도가 가장 높은 고유값을 찾아 최빈값으로 사용한다.
vals, counts = np.unique(discharge_arr, return_counts=True)
mode_val = vals[counts.argmax()]
print(f"최빈값: {mode_val}")최빈값: 11
(4) 방류량의 제1, 제3 사분위수를 계산하라.
답:
np.percentile() 함수에 분위수 인자로 백분율 (25와 75)을 지정하여 방류량의 제1, 제3 사분위수를 각각 계산한다.
Q1 = np.percentile(discharge_arr, 25)
Q3 = np.percentile(discharge_arr, 75)
print(Q1, Q3, sep='\n')11.0
16.0
(5) 클로로필-A 데이터의 범위를 계산하라.
답:
클로로필-A 데이터는 0번 열의 데이터다.
chl_a_arr = sc_weir_arr[:, 0]클로로필-A 데이터의 최솟값, 최댓값, 범위를 계산하여 출력한다.
print('min:', chl_a_arr.min())
print('max:', chl_a_arr.max())
print('범위:', chl_a_arr.max() - chl_a_arr.min())min: 51
max: 125
범위: 74
(6) 클로로필-A 데이터의 분산을 계산하라.
답:
np.var() 함수에서 ddof=0을 지정한다.
np.var(chl_a_arr, ddof=0)np.float64(506.8004000000001)(7) 클로로필-A 데이터의 표준편차를 계산하라.
답:
np.std() 함수에 ddof=0을 옵션으로 지정한다.
np.std(chl_a_arr, ddof=0)np.float64(22.51222778847087)(8) 클로로필-A 데이터를 min-max 스케일링한 후 sc_weir_arr의 새로운 열로 추가하라.
답:
(x - min) / (max - min) 공식으로 데이터를 정규화한 뒤, np.column_stack()을 사용하여 전체 데이터 배열에 새 열로 추가한다.
chl_a_min = chl_a_arr.min()
chl_a_max = chl_a_arr.max()
chl_a_scaled = (chl_a_arr - chl_a_min) / (chl_a_max - chl_a_min)
sc_weir_arr = np.column_stack([sc_weir_arr, chl_a_scaled])
sc_weir_arr[:5]array([[5.10000000e+01, 2.50000000e+01, 0.00000000e+00],
[5.10000000e+01, 2.50000000e+01, 0.00000000e+00],
[5.30000000e+01, 2.40000000e+01, 2.70270270e-02],
[5.30000000e+01, 2.40000000e+01, 2.70270270e-02],
[5.40000000e+01, 2.20000000e+01, 4.05405405e-02]])(9) 방류량 데이터를 표준화한 후 sc_weir_arr의 새로운 열로 추가하라.
답: (x - mean) / std 공식을 사용하여 방류량 데이터를 변환한 후, np.column_stack()을 사용하여 데이터 세트에
횡으로 결헙한다.
discharge_mean = discharge_arr.mean()
discharge_std = discharge_arr.std(ddof=0)
discharge_z = (discharge_arr - discharge_mean) / discharge_std
sc_weir_arr = np.column_stack([sc_weir_arr, discharge_z])
sc_weir_arr[:5]array([[5.10000000e+01, 2.50000000e+01, 0.00000000e+00, 1.58656273e+00],
[5.10000000e+01, 2.50000000e+01, 0.00000000e+00, 1.58656273e+00],
[5.30000000e+01, 2.40000000e+01, 2.70270270e-02, 1.42900933e+00],
[5.30000000e+01, 2.40000000e+01, 2.70270270e-02, 1.42900933e+00],
[5.40000000e+01, 2.20000000e+01, 4.05405405e-02, 1.11390253e+00]])